Capítulo 15.
La genética molecular de los procariotas y de los virus bacterianos
La información genética
esencial de los procariotas, de los cuales la bacteria E. coli es el ejemplo
mejor estudiado, está codificada en una molécula circular de DNA
de doble cadena asociada con una pequeña cantidad de RNA y proteínas
no histónicas. Se encuentra empaquetada en la región nucleoide
en la célula bacteriana.
En el curso de su larga historia
evolutiva, E. coli y otros procariotas han desarrollado procedimientos que les
permiten utilizar al máximo los nutrientesdestinados
al crecimiento celular. No producen todas las proteínas posibles al mismo
tiempo, sino sólo cuando se necesitan y en las cantidades necesarias.
En los procariotas la regulación de la síntesis de proteínas
tiene lugar principalmente a nivel de la transcripción aunque teóricamente
podría ocurrir en muchos puntos del proceso biosintético. La regulación
implica interacciones entre el ambiente químico de la célula y
proteínas reguladoras especiales, codificadas por genes reguladores.
La supervivencia a corto plazo de una célula procariótica depende del mantenimiento de la información genética y de la multiplicación de la célula que depende, a su vez, de una replicación rápida y precisa. En una escala de tiempo mayor, la aparición de variantes genéticas, de las que depende la evolución de las especies, es facilitada en gran medida por el reordenamiento ocasional de secuencias de DNA causado por la recombinación genética.
Existe un grupo de elementos
genéticos que son capaces de trasladarse de un lugar a otro insertándose
dentro del DNA. Estos elementos genéticos móviles son los plásmidos,
los virus y los transposones
Una vez incorporado a la célula, el DNA puede integrarse al cromosoma
por recombinación genética.
La transcripción y su
regulación
La replicación del DNA
comienza en un sitio particular del cromosoma y ocurre bidireccionalmente (replicación
theta). La transcripción consiste en la síntesis de una molécula
de mRNA usando como molde una de las hebras del DNA.
La replicación comienza
en una secuencia de nucleótidos específica, conocida como el origen
de replicación. Los puntos de origen y terminación de la replicación
se indican en rojo y en negro, respectivamente, y la cadena de DNA recién
sintetizada se muestra en rojo. A medida que las dos horquillas de replicación
se alejan del origen en direcciones opuestas, la DNA polimerasa añade
nucleótidos , uno por uno, al extremos 3' de las cadenas adelantada y
de los fragmentos de Okazaki de la cadena rezagada. Cuando el cromosoma bacteriano
circular se está replicando, forma una estructura que se asemeja a la
letra griega theta; así, su replicación se conoce como replicación
theta.
El proceso de transcripción
comienza cuando la enzima RNA polimerasa se acopla al DNA en el sitio específico
conocido como promotor. La molécula de RNA polimerasa se une estrechamente
al promotor y hace que la doble hélice de DNA se abra, iniciándose
la transcripción. La cadena de RNA en crecimiento permanece brevemente
unida por puentes de hidrógeno al DNA molde, (sólo 10 o 12 ribonucleótidos
están unidos al DNA en cualquier instante dado) y luego se desprende
como una cadena simple.
Un segmento de DNA que codifica un polipéptido se conoce como gen estructural. Frecuentemente, los genes estructurales que codifican polipéptidoscon funciones relacionadas se presentan juntos formando una sucesión en el cromosoma bacteriano. Estos grupos funcionales podrían incluir, por ejemplo, dos cadenas polipeptídicas que juntas constituyen una enzima particular o tres enzimas que trabajan en una única vía enzimática.
Los grupos de genes que codifican esas moléculas suelen transcribirse en una única cadena de mRNA. Estos mRNA se conocen con el nombre de mRNA policistrónicos mientras que, los que poseen información para un único polipéptido, se denominan monocistrónicos. Así, un grupo de polipéptidos que la célula necesite al mismo tiempo pueden ser sintetizados juntos, constituyendo una manera simple y eficiente de controlar su coexpresión.

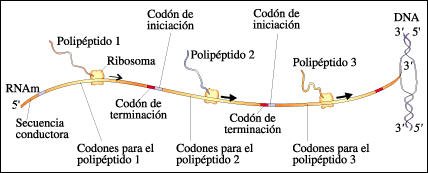
Esquema del proceso de transcripción en los procariotas
En los procariotas, la transcripción
a menudo da como resultado una molécula de mRNA con secuencias que codifican
varias cadenas polipeptídicas diferentes (mRNA policistrónico).
Las secuencias están separadas por codones de terminación y de
iniciación. En este diagrama, los codones de terminación y de
iniciación son contiguos pero, en algunos casos, pueden estar separados
por hasta 100 a 200 nucleótidos. El extremo 5' de la molécula
de mRNA tiene una secuencia conductora corta y el extremo 3' tiene una secuencia
cola; ninguna de estas secuencias codifica proteínas. La traducción
generalmente comienza en el extremo conductor de la molécula de mRNA,
mientras que el resto de la molécula aún está siendo transcripta.
La molécula de mRNA recién
sintetizada tiene una corta secuencia "guía" en su extremo
5', la secuencia de Shine-Dalgarno, que es la que se une al ribosoma. La región
codificadora de la molécula es una secuencia lineal de nucleótidos
que dicta con precisión la secuencia lineal de aminoácidos en
cadenas polipeptídicas determinadas. Puede haber varios codones de terminación
e iniciación dentro de la molécula de mRNA, marcando el fin de
un gen estructural y el comienzo del siguiente, respectivamente. Cada uno de
los codones de iniciación tiene que estar precedido por un sitio de unión
al ribosoma. Una secuencia adicional de nucleótidos en el extremo 3'
se conoce como "cola". Los ribosomas se acoplan a la molécula
de mRNA aun antes de que la transcripción se haya completado.
La regulación implica
interacciones entre el ambiente químico de la célula y proteínas
reguladoras especiales, codificadas por genes reguladores. Por ejemplo, las
células de E. coli abastecidas con el disacárido lactosa como
fuente de carbono y energía, requieren de la enzima beta-galactosidasa
para escindir ese disacárido. Las células que crecen en un medio
con lactosa fabrican aproximadamente 3.000 moléculas de beta-galactosidasa.
Sin embargo, en ausencia de lactosa hay un promedio de una molécula de
enzima por célula. En conclusión, la presencia de lactosa provoca
la induccción de la producción de las moléculas de enzima
necesarias para degradarla. Se dice, entonces, que estas enzimas son inducibles.
Por el contrario, la presencia de un nutriente determinado puede inhibir la transcripción de un grupo de genes estructurales. La E. coli, como otras bacterias, puede sintetizar cada uno de sus aminoácidos a partir de amoníaco y de una fuente de carbono. Los genes estructurales que codifican las enzimas necesarias para la biosíntesis del aminoácido triptófano, por ejemplo, están agrupados y se transcriben en una única molécula de mRNA. Este mRNA es producido continuamente por células en crecimiento si el triptófano no está presente. En presencia de triptófano, se detiene la producción de las enzimas. Estas enzimas, cuya síntesis se reduce en presencia de los productos de las reacciones que catalizan, se denominan represibles.
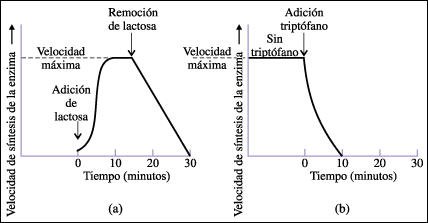
Enzimas inducibles y represibles.
a. La velocidad de síntesis
de beta-galactosidasa, una enzima inducible producida por E. coli, se incrementa
dramáticamente cuando se añade lactosa al medio de crecimiento
circundante. En tanto la lactosa sea abundante en el medio, la producción
de enzima continúa a su velocidad máxima. Sin embargo, cuando
se elimina la lactosa del medio, la velocidad de síntesis de beta-galactosidasa
cae inmediatamente.
b. En ausencia de un sustrato esencial, como el aminoácido triptófano,
las enzimas requeridas para su producción se sintetizan a velocidad máxima.
Sin embargo, si se añade
triptófano al medio, la síntesis de estas enzimas se reprime rápidamente.
Un medio principal de regulación genética en las bacterias es
el sistema operón. Un operón comprende al promotor, a los genes
estructurales y al operador.
Los genes estructurales del
operón codifican un grupo de proteínas funcionalmente relacionadas
y se transcriben como una sola molécula de mRNA. La transcripción
es controlada por secuencias en el promotor y en el operador, adyacentes a los
genes estructurales y capaces de unir proteínas específicas. El
promotor contiene un sitio de unión para la RNA polimerasa y puede contener
un sitio de unión para el complejo CAP-AMP cíclico. El operador
es el sitio de unión para un represor, proteína codificada por
otro gen, el regulador, que puede estar localizado a cierta distancia en el
cromosoma bacteriano. El operador se puede superponer con el promotor, con el
primer gen estructural, o con ambos; cuando el represor se une a la molécula
de DNA en el sitio operador, la RNA polimerasa no puede iniciar la transcripción
del mRNA. Cuando el represor no está presente, la RNA polimerasa puede
unirse al DNA y comenzar su movimiento a lo largo del cromosoma, permitiendo
que ocurra la transcripción y la síntesis de proteínas.
El operón lac es un ejemplo
de un operón inducible. Pasa de "desconectado" a "conectado"
cuando un inductor se une al represor y lo inactiva. Otros operones, como el
operón trp, son represibles. Estos pasan de "conectado" a "desconectado"
por la acción de un correpresor, que se une a un represor inactivo. Éste
activa al represor y se une al operador. Tanto la inducción como la represión
son formas de regulación negativa.
La regulación positiva de algunos operones la suministra la unión del complejo CAP-cAMP. Por ejemplo, cuando hay glucosa en la célula, los niveles de AMP cíclico son bajos y el complejo CAP-cAMP no se forma. Cuando la glucosa se agota, aumentan los niveles de cAMP y se forman complejos CAP-cAMP que se unen luego al promotor. Con la lactosa presente (y el represor así inactivado) y el complejo CAP-cAMP en su lugar, la RNA polimerasa también se une al promotor y ocurre la transcripción desde el operón.
En un operón, la síntesis
de proteínas está regulada por interacciones que involucran a
un represor y a un inductor o bien a un represor y a un correpresor.
a. En los sistemas inducibles,
como el operón lac, la molécula del represor es activa, hasta
que se combina con el inductor (en este caso, alolactosa).
b. En los sistemas represibles, como el operón trp, el represor se activa
sólo cuando se combina con el correpresor.
Los operones inducibles y represibles son ambos desconectados por proteínas represoras codificadas por genes reguladores. El represor se une al DNA en el operador y evita, de esta forma, que la RNA polimerasa inicie la transcripción.
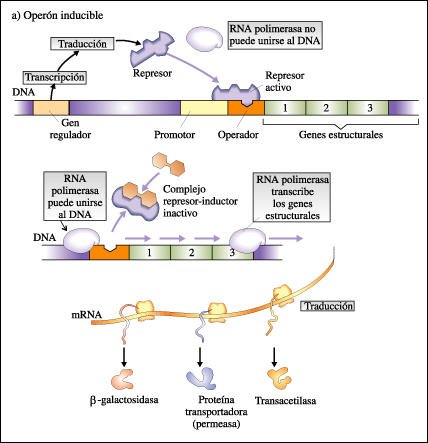
En los operones inducibles, el inductor contrarresta el efecto del represor uniéndose a él y manteniéndolo en una forma inactiva. Así, cuando el inductor está presente, el represor ya no puede unirse al operador y pueden proseguir la transcripción y la traducción.
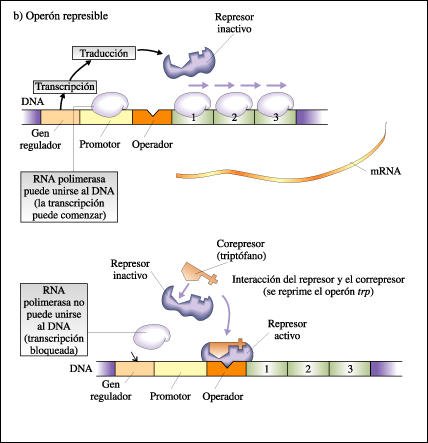
En los operones represibles, en ausencia del correpresor, el represor se encuentra inactivo. En este estado, la transcripción y la traducción ocurren permanentemente. En presencia de un correpresor, se forma un complejo represor-correpresor y el represor se activa. Así puede unirse al operador bloqueando la transcripción.
Elementos genéticos móviles
Los elementos genéticos
móviles son los plásmidos, los virus y los transposones.
Además de los genes que
lleva el cromosoma bacteriano, las bacterias pueden contener otros genes llevados
en los plásmidos, que son moléculas de DNA de doble cadena mucho
más pequeñas y también circulares. La mayoría de
los plásmidos pueden ser transferidos de célula a célula.
Esta transferencia de DNA por contacto célula a célula se conoce
como conjugación. Parte de los plásmidos puede integrarse reversiblemente
al cromosoma bacteriano, en cuyo caso se conocen como episomas.
El factor F (de fertilidad) de E. coli es un plásmido presente en las células F+ dadoras (machos) y puede ser transferido a las células F- (hembras) receptoras; estas células pueden transformarse en F+ y transferir, a su vez, el factor F. Cuando el factor F se integra al cromosoma de una célula de E. coli (transformándolas en una célula Hfr), parte del cromosoma o (en raras ocasiones) todo el cromosoma puede ser transferido a otra célula de E. coli por conjugación. En el momento de la transferencia, el cromosoma se replica por el mecanismo de círculo rodante y una copia de DNA de cadena simple entra a la célula receptora linealmente, de modo que los genes bacterianos penetran uno tras otro, en una secuencia fija. Luego se sintetiza la cadena complementaria. Como la velocidad a la cual los genes bacterianos entran en la célula receptora es constante a una temperatura dada, la separación a intervalos regulares de las células que se conjugan permite mapear el cromosoma bacteriano.
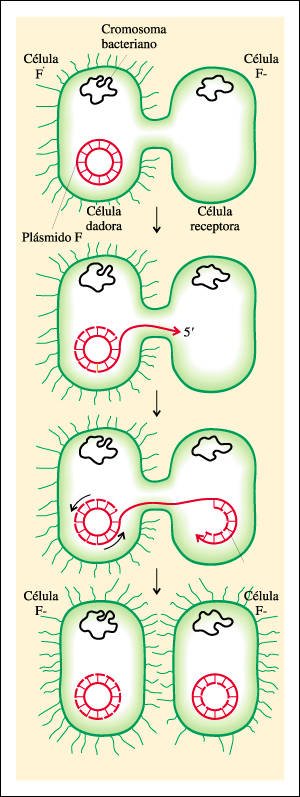
Transferencia de un plásmido F de una célula F+ a una célula F-, por medio de la conjugación. En estos diagramas, el plásmido se muestra muy aumentado; en realidad, su tamaño es mucho menor que el del cromosoma bacteriano, ya que contiene muchos menos pares de nucleótidos.
Una cadena única de DNA se mueve desde la célula dadora hacia la célula receptora, donde posteriormente se sintetiza su cadena complementaria (líneas punteadas en el cromosoma de la célula receptora). A medida que la cadena de DNA se transfiere, la cadena de la célula dadora "gira" en sentido contrario a las agujas del reloj, exponiendo los nucleótidos desapareados. Éstos sirven como molde para la síntesis de una cadena complementaria de DNA (líneas punteadas, célula dadora). Como resultado, el plásmido en la célula dadora continúa siendo un círculo de DNA de doble cadena y el plásmido transferido convierte a la célula receptora en una célula F+. Este mecanismo de replicación del DNA del plásmido se conoce como "replicación en círculo rodante".
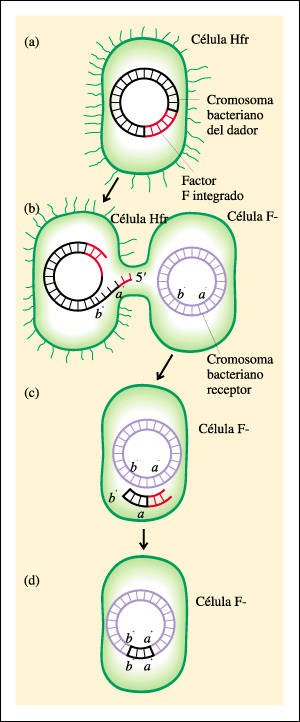
Transferencia de una porción del cromosoma bacteriano durante la conjugación.
a. Una célula F+ se convierte
en una célula Hfr cuando el plásmido F se inserta en su cromosoma.
b. Ocurre una ruptura en la
secuencia del factor F integrado al cromosoma y comienza la replicación
en círculo rodante. Liderada por su extremo 5', una cadena simple de
DNA, que contiene una porción de la secuencia del factor F seguida por
los genes a+ y b+, penetra en la célula F-. En este ejemplo, sólo
una porción del cromosoma se transfiere antes de que las células
se separen una de otra.
c. El fragmento de DNA transferido
es homólogo a la parte del cromosoma receptor que lleva los mismos genes.
La "concordancia", sin embargo, no es exacta, dado que los genes a-
y b- son formas alternativas de los genes a+ y b+. Difieren en la secuencia
de nucleótidos como resultado de mutaciones que han hecho, en este ejemplo,
que a y b sean no funcionales, o sea, que no den como resultado la síntesis
de los productos a y b.
d. Ocurre la recombinación
entre el DNA dador y el cromosoma receptor. La célula hija que contenga
los genes transferidos a+ y b+ será capaz de sintetizar los productos
a y b. Esto ofrece un medio por el cual puede demostrarse la conjugación.
Nótese que la célula dadora sigue siendo Hfr y que la célula
receptora aún es una F-, al igual que sus células hijas.
Otros elementos genéticos
móviles son los virus bacterianos o bacteriófagos; están
formados por DNA o RNA envuelto en una cubierta proteínica. Dentro de
la célula hospedadora, el ácido nucleico viral puede utilizar
los recursos metabólicos de la célula para sintetizar más
moléculas de ácido nucleico viral y más proteínas
virales. Empaquetados en sus cubiertas proteínicas, las partículas
de virus pueden provocar la lisis celular y escapar de la célula (ciclo
lítico) para comenzar un nuevo ciclo de infección.
El DNA de algunos virus, conocidos
como virus atenuados, puede integrarse en el cromosoma del hospedador de la
misma manera que un episoma y replicarse junto con el cromosoma iniciando un
ciclo lisogénico. Cuando se integra en un cromosoma hospedador, el DNA
de un virus bacteriano se conoce como profago. De tanto en tanto, los profagos
se separan del cromosoma y establecen un nuevo ciclo de infección.
Los virus pueden servir como vectores de material genético, transportando genes de una célula a otra, proceso conocido como transducción. La transducción general ocurre cuando el DNA hospedador, fragmentado en el curso de la infección viral, se incorpora a nuevas partículas virales que llevan estos fragmentos a una nueva célula hospedadora. La transducción especializada ocurre cuando un profago, al liberarse del cromosoma hospedador, lleva con él, como parte del cromosoma viral, genes del hospedador que luego son transportados a una nueva célula hospedadora.
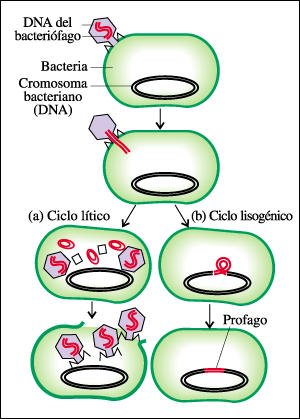
Cuando ciertos tipos de virus infectan bacterias, puede ocurrir uno de dos hechos: que comience una infecció o que el virus se integre al cromosoma bacteriano.
a. El DNA viral puede entrar
a la célula y comenzar una infección (ciclo lítico); o
b. el DNA viral puede incorporarse
al cromosoma bacteriano, replicarse con él y ser transferido a las células
hijas (ciclo lisogénico).
Las bacterias que albergan a
estos virus se conocen como lisogénicas porque, de cuando en cuando,
los profagos se activan y establecen un nuevo ciclo lítico.
Los transposones son elementos
genéticos móviles que difieren de los plásmidos y de los
virus en varios aspectos:
1. llevan un gen para la enzima
transposasa, que cataliza su integración al cromosoma del hospedador;
2. en cada extremo del transposón
hay una secuencia repetida directa o invertida;
3. la secuencia blanco en el
cromosoma hospedador se duplica cuando se inserta el transposón y el
resultado es que el transposón queda flanqueado en cada extremo por la
secuencia blanco.
Los transposones pueden causar mutaciones, interfiriendo con la expresión normal de los genes de la célula hospedadora. Los transposones simples contienen solamente genes implicados en su transposición; los compuestos llevan genes estructurales adicionales.
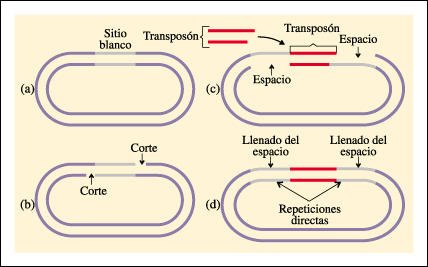
Inserción de un transposón en un DNA receptor.
a. La secuencia de nucleótidos
en la cual ocurre la inserción se conoce como sitio blanco.
b. Se producen cortes escalonados
en el sitio blanco y
c. el transposón se une
a los extremos que sobresalen de los cortes.
d. Cuando los espacios se completan
por síntesis de la hebra complementaria, se forman repeticiones idénticas
en ambos lados del transposón insertado. Éstos, a menudo, se usan
como "mojones" para identificar las secuencias de DNA que han sido
transpuestas.
Estrategias de recombinación
En ocasiones, DNA foráneo,
portador de información, puede introducirse en una célula bacteriana.
Las bacterias portadoras de estas secuencias de DNA pueden transmitir los plásmidos,
transposones o profagos adquiridos a las células hijas durante la división
celular por transferencia vertical.
El DNA incorporado a la célula
puede integrarse al cromosoma por recombinación genética.
Existen dos grandes tipos de
recombinación: la recombinación general u homóloga y la
recombinación específica de sitio.
La recombinación homóloga implica el intercambio entre segmentos homólogos de DNA. Cuando dos segmentos homólogos de DNA de doble cadena se alinean uno con otro, pueden ocurrir intercambios entre las moléculas de modo tal que los genes pueden ser transferidos de una molécula a otra. Este fenómeno se produce en las células eucarióticas en la meiosis, durante el crossing-over; también ocurre entre el DNA de la célula receptora y el de la célula dadora, luego de la conjugación, la transformación y la transducción en las células bacterianas. Se han propuesto varios modelos para explicar cómo ocurre la recombinación entre homólogos; uno de ellos es el "intercambio de cadena simple".
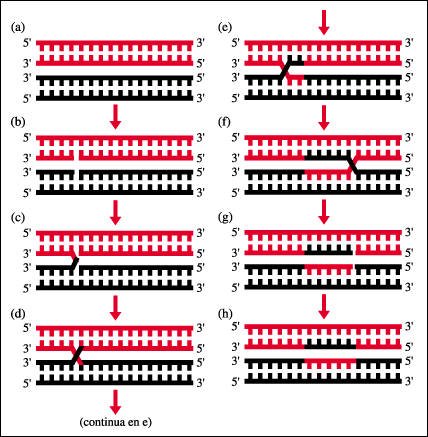
El modelo "intercambio de cadena simple" de la recombinación genética entre dos cadenas homólogas de DNA.
a. El DNA de cada uno de los
progenitores homólogos se indican en negro y el otro en color rojo.
b. Se rompe una cadena de cada
molécula de DNA,
c. que se intercambia con la
cadena homóloga de la otra molécula y
d. ídem,
e. se une a la cadena intercambiada.
f. El intercambio de cadenas
entre los DNA ocurre a lo largo del DNA y
g. en un punto específico,
las cadenas intercambiadas se rompen nuevamente y
h. se resellan, completando
el intercambio y la recombinación de los genes.
Un segundo tipo de recombinación,
la llamada recombinación específica de sitio, implica la inserción
de elementos genéticos móviles (y removibles), como el plásmido
F. Estos elementos pueden entrar o salir del DNA de un cromosoma a través
de un evento de recombinación. Esta recombinación involucra secuencias
específicas del DNA del fago o del plásmido y del DNA bacteriano,
que incluyen una pequeña región de homología y enzimas
de recombinación especificas. Un tipo diferente de recombinación,
que no involucra ningún tipo de homología de secuencia, es la
implicada en la inserción de los transposones. La transposasa, enzima
responsable de la inserción, introduce cortes en el DNA cromosomal, en
secuencias blanco al azar.